|
SIS: Système
"Susceptible - Infectieux" en épidémiologie
B. Bonté, P. Bommel
Un modèle SIS (Système Susceptible - Infecté) simple, qui
permet aux utilisateurs de comparer 3 types de paradigmes
sur un même modèle simple en épidémiologie : équations
différentielles continues, modèle discret et plusieurs
implémentations d'un SMA.
Objectif
Il s'agit d'une réplication d'un modèle épidémiologique
standard qui simule la propagation d'une épidémie dans une
société : des personnes en bonne santé (également appelées
Susceptibles) peuvent
devenir malades (Infectées)
lorsqu'elles entrent en contact avec d'autres personnes
déjà porteuses de la maladie. À leur tour, elles
contribuent à la propagation de la maladie lorsqu'elles
rencontrent d'autres personnes.
Dans ce modèle, la maladie n'est pas dangereuse. Au bout
d'un certain temps, les personnes infectées redeviennent
susceptibles.
Une simulation doit donc surveiller le nombre de personnes
infectées et de personnes en bonne santé au fil du temps.
Ce modèle présente deux versions principales :
Version 1: modèle global (équations différentielles)
Dans la première variante, la version "globale", les
individus ne sont pas représentés, mais seulement les
populations de Susceptibles
et Infectés :

S: nombre d'individus susceptibles. I: nombre d'individus infectés.
β: taux d'infection (0,3). γ: taux de récupération (0,1)
Ce schéma correspond à un système à 2 équations
différentielles :
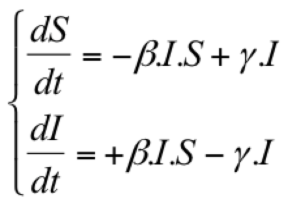
Ce modèle continu peut être discrétisé en transformant dt
en deltaT :
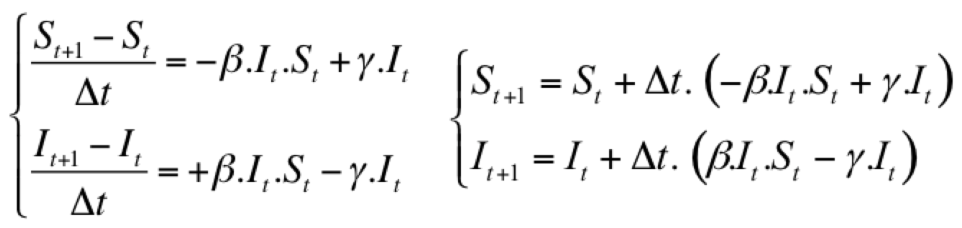
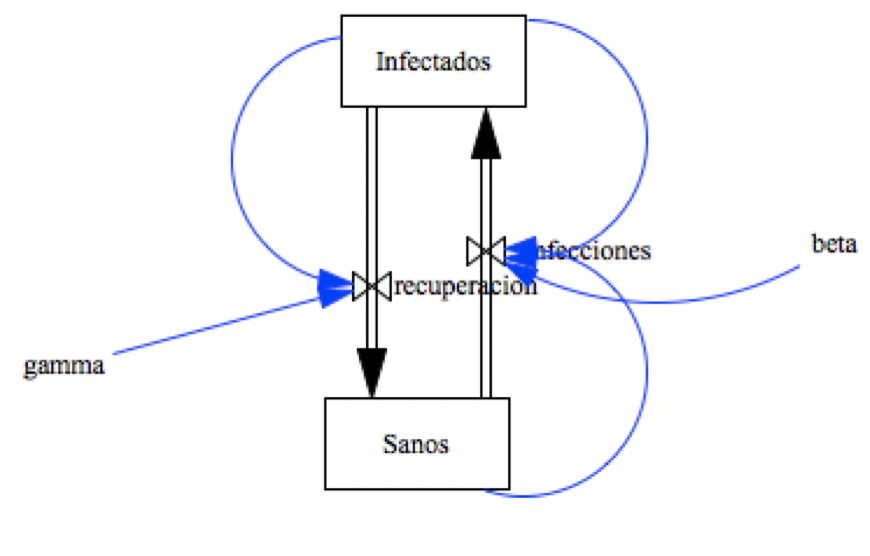
Vue du modèle sous Vensim
(modèle "stock & flow") :
La figure suivante montre des simulations avec Vensim
à partir de 3 états initiaux différents :
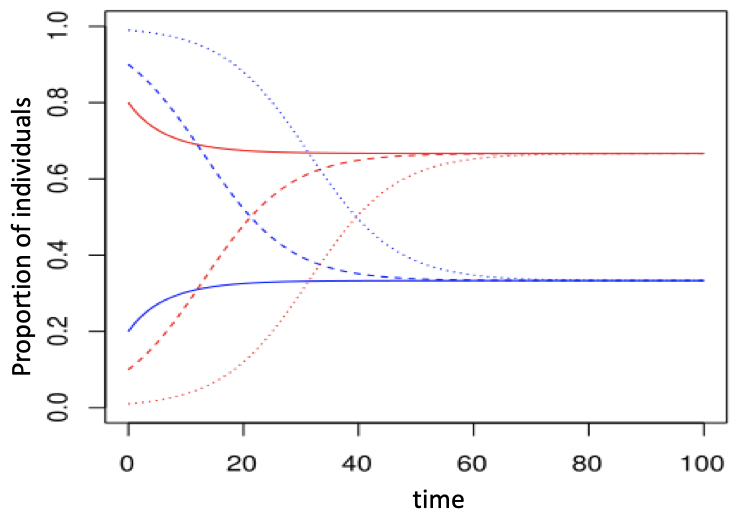
A noter que à l'équilibre :
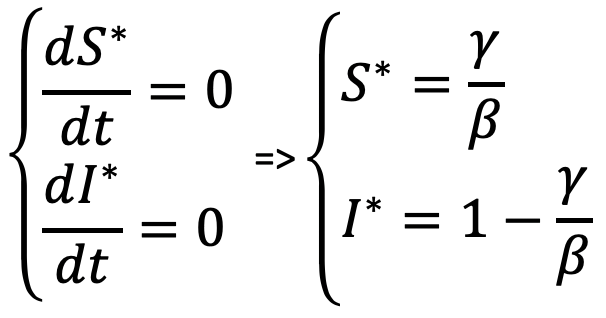 Au bout d'un certain
temps, S et I sont stables ; leur niveau dépend uniquement
de β et γ : S*=1/3 and I*=2/3 Au bout d'un certain
temps, S et I sont stables ; leur niveau dépend uniquement
de β et γ : S*=1/3 and I*=2/3
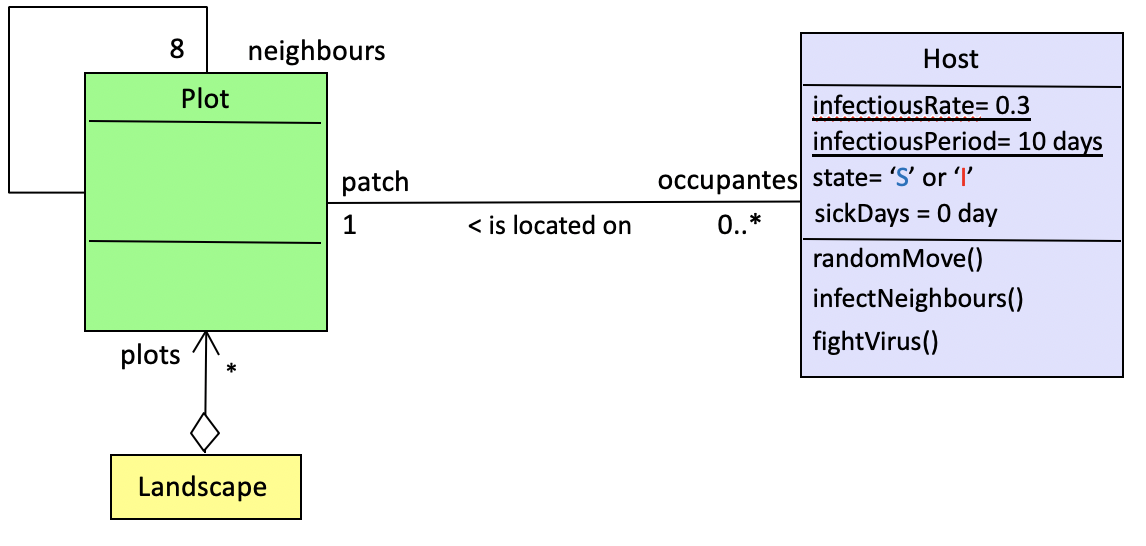
Version 2: ABM
La deuxième variante, "ABM", représente explicitement les
individus du système.
Le taux d'infection (β = 0,3, défini au niveau populationnel)
devient désormais une probabilité individuelle d'être
infecté au contact d'un autre agent infecté (30 %). Le
taux de guérison doit également être adapté au niveau
individuel. Par exemple, il peut être transformé en une
Période Infectieuse de 10 jours. Après cette période,
l'agent malade se rétablit. En d'autres termes, le taux de
guérison (10 %, défini au niveau de la population) se
traduit par une période de guérison de 10 jours, définie
au niveau individuel.
Lorsqu'ils se déplacent dans le paysage, les agents
peuvent se rencontrer au hasard. Afin d'avoir une
probabilité de rencontre équivalente à celle du modèle
global, la taille de l'espace doit être calculée en
fonction de la taille de la population.
Le paramètre ß (taux d'infection : 0,3) peut être exprimé
sous la forme :
ß = -k log(1 - c) , où
* k est le nombre moyen de contacts
entre deux personnes par unité de temps, et
* c est la probabilité que le contact
entre un individu sensible et un individu infectieux
entraîne une infection. Donc c est égal au taux
d'infection (= 0,3).
En fixant c à 0,3, nous calculons k = -ß / log(1 - c) =
-0,3 / log (0,7) = -0,3 / (0,7 log) = 1,93671
Il y a en moyenne 1,93671 contacts entre deux personnes
par étape.
Ainsi, pour un voisinage de 8 (Moore), 1 agent a 1 chance
sur 8 d'aller sur la cellule d'un agent voisin.
Si X.Y est la taille de la grille, alors
popSize = k * X.Y/ 8 <=>
X.Y = popSize * 8 /k
Dans Cormas, cette implémentation permet de représenter
une grille spatiale avec les agents situés :
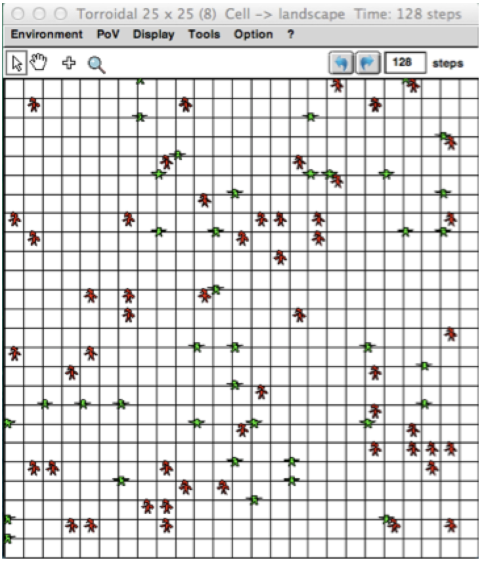
Mais cette transformation du modèle global (éq.
différentielle) en un SMA correspond à une façon de faire
(le scénario No Spatial, Infectious Period). Il peut
être défini différemment, comme présenté dans ce qui suit
:
Implémentions et comparaison des scenarios suivants
En utilisant le modèle SIS dans Cormas, vous pouvez
choisir un scénario parmi 7 :
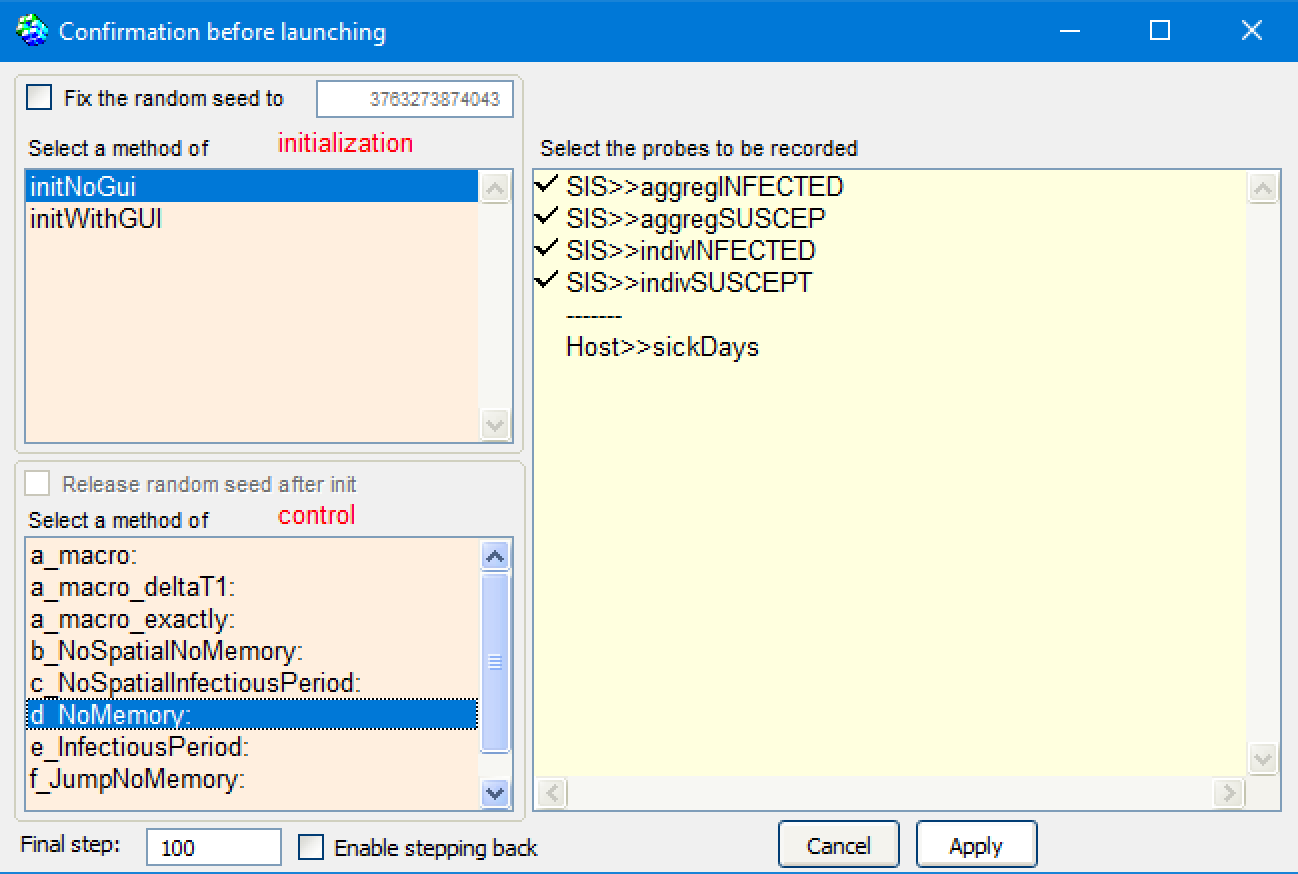
Pour chaque scénario, les résultats du modèle à équations
discrètes (modèle global) et du modèle SMA (modèle local)
peuvent être comparés (aggregINFECTED vs indivINFECTED).
Ils sont initialisés avec au moins 1000 hôtes.
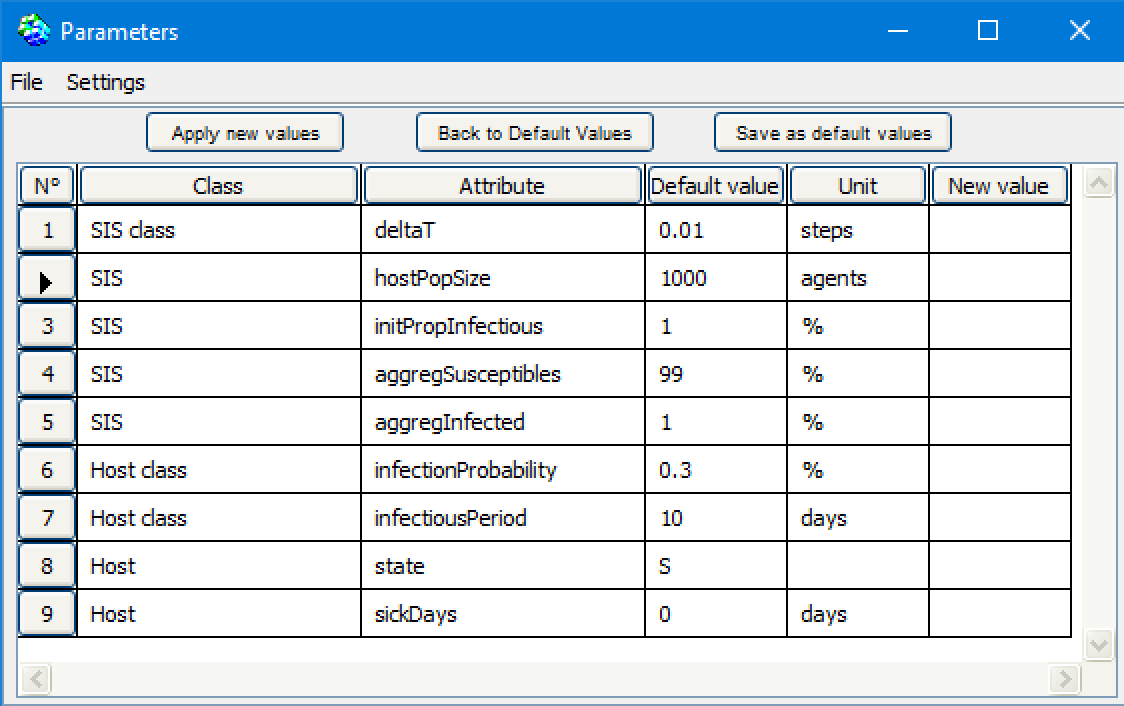
Tous les paramètres sont présentés dans cette table:
a) macro
Ici, les agents ne font rien, ou plutôt ne décident de
rien. Leur état est modifié par un opérateur extérieur :
c'est le résultat du modèle global.
Dans cette version (a_macro_deltaT1), le modèle calcule le
nombre d'agents infectés et susceptibles selon l'équation
discrète avec delta T = 1.
Les sorties sont comparées avec celles du modèle global
discret avec un deltaT fixé à 0.01 :
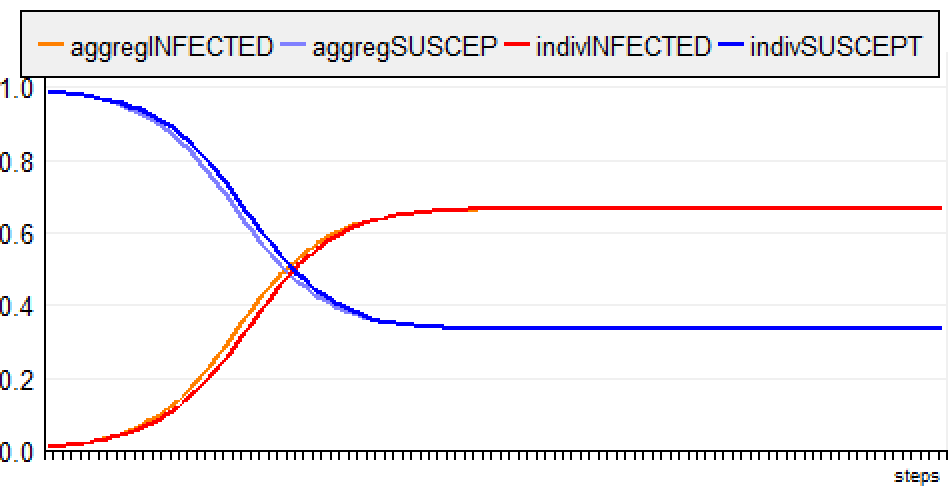
Ici, les courbes pour les deux scénarios (agrégés et
individuels) sont quasi similaires, ce qui est logique.
La petite différence est due à la résolution du temps:
deltaT = 1 dans le cas de l'ABM et deltaT = 0.01 pour le
modèle global.
b) No Spatial, No Memory
Les agents ne sont pas situés. Ils se rencontrent au
hasard. On traduit cela de la façon suivante : chaque
agent infecté peut rencontrer un des autres agents pris
aléatoirement dans la population. Si ce dernier est
Susceptible, alors il peut devenir infecté avec une
probabilité donnée (infectionProbability = 0.3).
Lorsqu'il est infecté, un agent a une probabilité de 10 %
de se rétablir chaque jour.
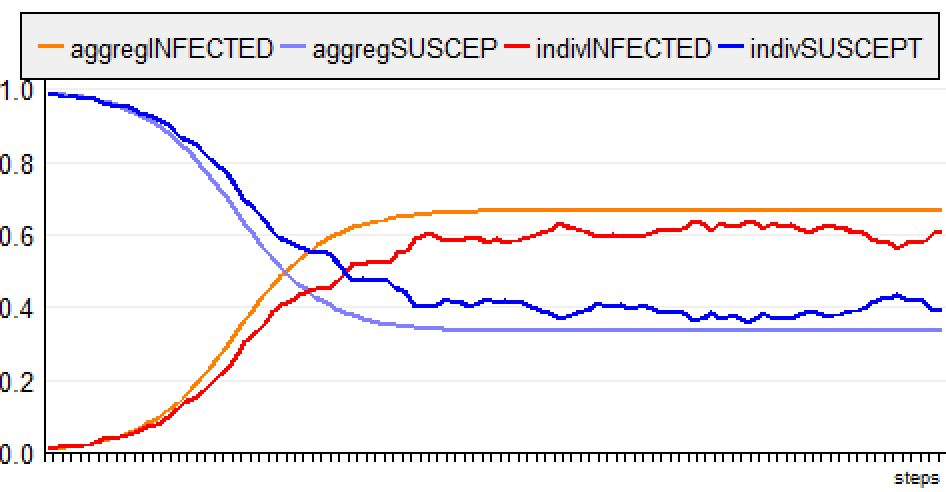
Pour la version ABM, l'évolution de la maladie est un peu
plus lente que pour le modèle global et le taux
d'infection se stabilise autour 0.6 (au lieu de 0.666).
c) No Spatial, Infectious Period
Les agents ne sont pas situés. Ils se rencontrent au
hasard. Lorsqu'il est infecté, un agent est contagieux
pendant 10 jours.
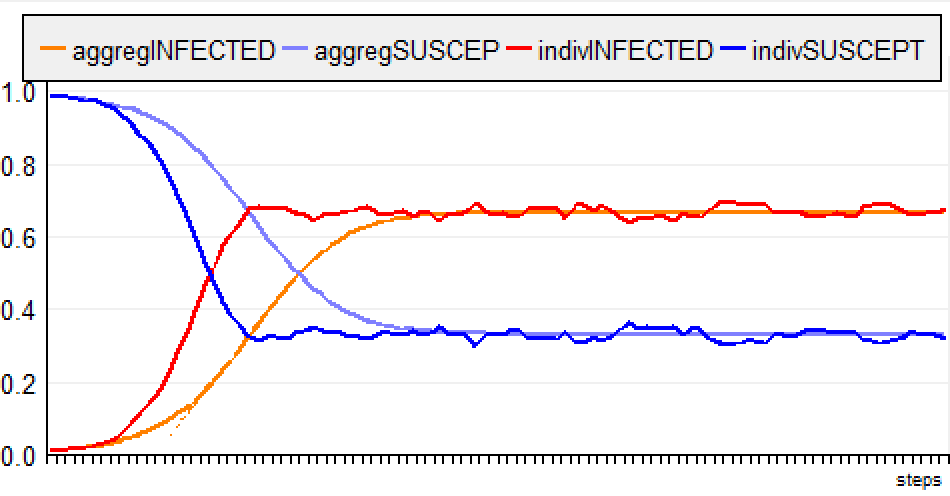
Pour la version ABM, l'évolution de la maladie est plus
rapide, mais le taux d'infection se stabilise autour de
0.666 (comme pour le modèle global).
d) NoMemory
Les agents sont situés sur une grille (pour 1000 agents,
la dimension spatiale est fixée à 65x64 cellules = 4160
cellules). Ils peuvent se rencontrer lorsqu'ils se
déplacent au hasard.
Lorsqu'il est infecté, un agent a une probabilité de 10 %
de se rétablir chaque jour.
Le step général du modèle (et pour les scénarios suivants)
est divisé en 3 phases :
1) Tous les agents bougent,
2) Les agents infectés peuvent infectés leurs
voisins localisés sur la même cellule, avec
infectionProbability),
3) Les agents infectés combattent le virus
(probabilité de guérir de 10% à chaque step)
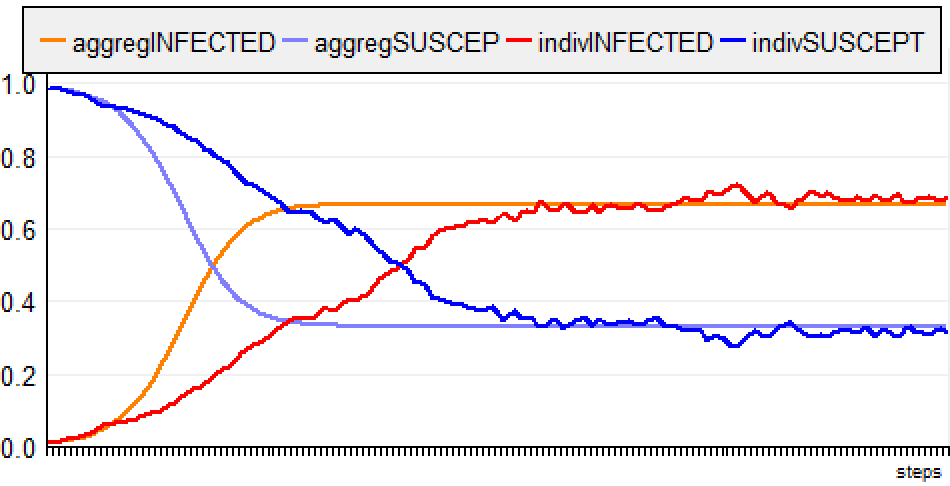
(la simulation est exécutée sur 150 steps, afin de
vérifier que les courbes sont finalement alignées avec
l'état d'équilibre).
Pour la version ABM, l'évolution de la maladie est bien
plus lente, mais mais le taux d'infection se stabilise
autour de 0.666 (comme pour le modèle global).
e) Infectious Period
Les agents sont situés et se déplacent de manière
aléatoire. Lorsqu'il est infecté, un agent est contagieux
pendant 10 jours.
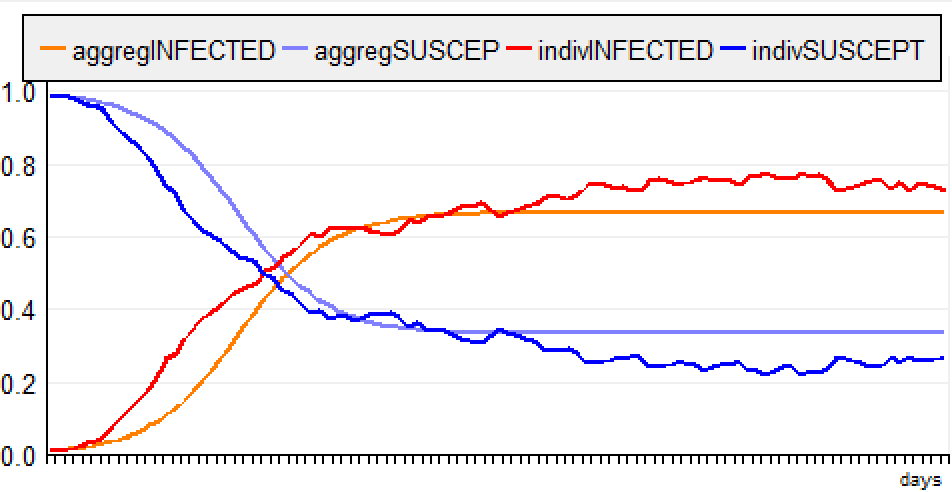
f) Jump NoMemory
Les agents sont localisés et sautent aléatoirement à un
autre endroit de la grille. Lorsqu'il est infecté, un
agent a une probabilité de 10 % de se rétablir chaque
jour.
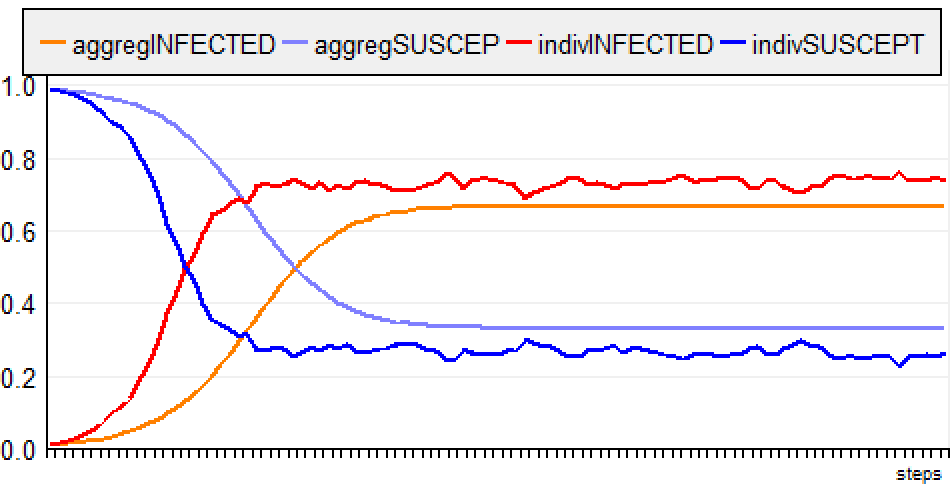
g) Jump, Infectious Period
Les agents sont situés et sautent aléatoirement à un autre
endroit de la grille. Lorsqu'il est infecté, un agent est
contagieux pendant 10 jours.
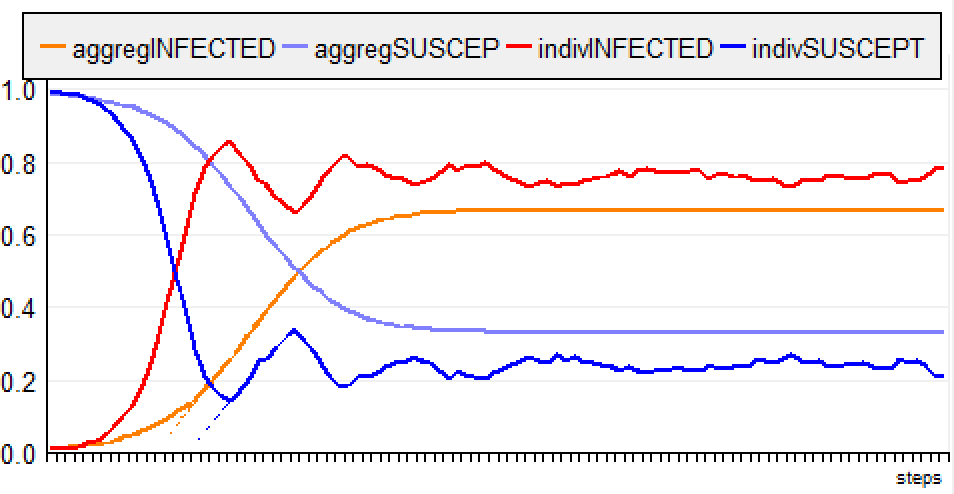
Enfin, la figure suivante permet de comparer un modèle
similaire conçu selon 3 types de paradigmes : équation
différentielle continue (lignes épaisses), équation
différentielle discrète (lignes fines) et ABM-e (lignes
pointillées) :
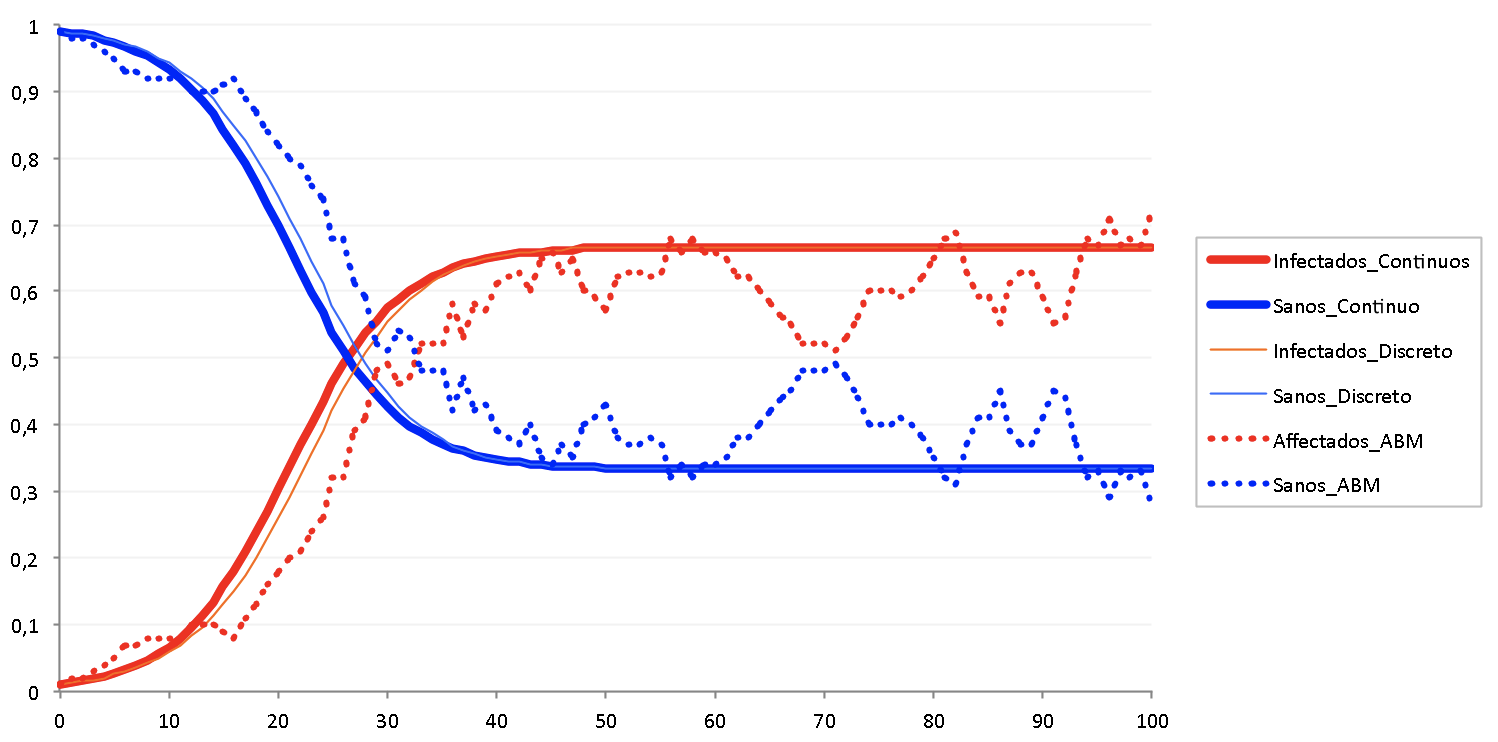
Conclusion
Même pour un modèle très simple, il existe plusieurs
façons de le formaliser, ce qui conduit souvent à des
simulations similaires mais non identiques. Pour les deux
modèles "globaux" (équations différentielles continues et
discrètes), on constate déjà de petites différences
lorsque le delta T = 1 (cf. figure précédente).
La traduction de ce modèle en un SMA nécessite des
ajustements (pour passer du global au local) avec des
conséquences sur les résultats des simulations.
Dans le contexte du Covid-19, des initiatives similaires
de modélisation didactique ont été menées, avec Gama (https://gama-platform.github.io/covid19)
et avec Netlogo (https://covprehension.org/, en
français).
|
|

